Ocurre en tres etapas:
1ª etapa: desenrrollamiento y apertura de la doble hélice.en el punto ori.
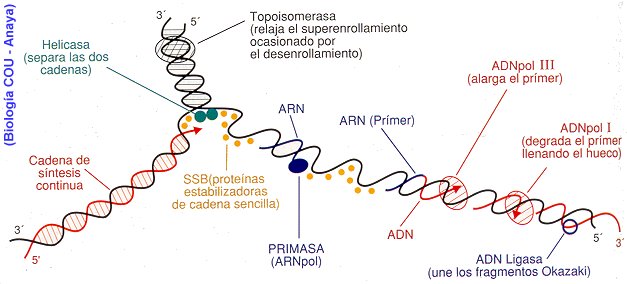
En el punto de origen u ORI, que es un lugar del cromosoma con gran contenido de A y T, la doble hélice se abre, mediante la DNA helicasa y las proteínas desestabilizadoras de la hélice o proteínas de unión a DNA de una sola cadena, vuelven recta la cromatina y la mantienen abierta. La DNA polimerasa sintetiza las cadenas complementarias a cada una de las cadenas primitivas. Forma dos copias activas de ADN, una es continua, o sea, basta con agregar los nucleotidos correspondientes porque la hebra antigua tiene 3', por lo que se crea una 5´. En la otra hebra, se produce un proceso discontinuo, debido a que la hebra quedo con un final 5', debiendo partir con un 3', y la célula es incapaz de seguir la cadena con este final, para que se inicie la copia del DNA hace falta un corto RNA específico (10 pares de bases), denominado RNA cebador, que hace que empiece a actuar la DNA polimerasa. El RNA cebador es generado por la RNA primasa (sintetizadora de RNA). Esta enzima se une directamente a la DNA helicasa, formando un complejo llamada primosoma, que se va desplazando con la cadena en formación. Conforme van existiendo fragmentos de cadena abiertos de suficiente longitud, se va sintetizando la cadena discontinua formando pequeños fragmentos, denominados Fragmentos de Okazaki, cada uno de unos 1000 nucleótidos. . Hace falta un RNA cebador por cada fragmento de Okazaki. La RNA primasa, va sintezando a intervalos los RNA cebadores que van siendo incorporados a la copia como si fueran ADN, entre los fragmentos de Okazaki, hasta que se alcanza el RNA cebador del fragmento de Okazaki ya terminado. . La cadena con ARN cebador, es denominada cadena retrasada.
Las enzimas ligasas son las encargadas, despues, de ir arreglando los nicks cuando se sustituye el ARN cebador.

No hay comentarios:
Publicar un comentario